生存分析是非常重要的表型,诸多文章均有介绍。 其中,最权威的是生存分析数据库是Kaplan-Meier (KM) Plotter(http://kmplot.com/analysis/),能够评估21种肿瘤中54000个基因对生存率的影响。数据库中研究最多的肿瘤数据集包括乳腺癌(6234例)、卵巢癌(2190例)、肺癌(3452例)和胃癌(1440例)。miRNA系统包括20种不同肿瘤类型的11000个样本。该系统包括基因芯片和RNA-seq来源的数据,数据库包括GEO、EGA和TCGA,基于荟萃分析(meta-analysis)发现和评估生存标记物的价值。
此外,PrognoScan是生存分析信息最全面的数据库,主要数据来源是GEO,结果中均含有GSE序列号,网址:http://dna00.bio.kyutech.ac.jp/PrognoScan/index.html。
PrognoScan页面相对简单,操作也不复杂。PrognoScan分析生存率,登录官网,在对话框中输入基因名称,点击submit。关键是数据的整理。

然后出现下表。点击cox p value一栏,使得数据按照cox p从小到大的顺序排列,以获得具有显著差异的生存分析数据。
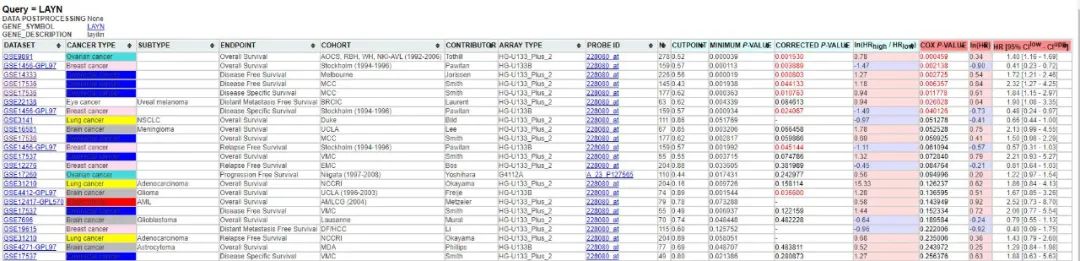
根据肿瘤类型,cox p value的结果,点击探针Probe ID(蓝色划线,可以点击进去)。出现类似下图结果,可以下载,文章需要的是kaplan-Meier plot数据。截图后在PPT中标注相应信息即可,非常简单。
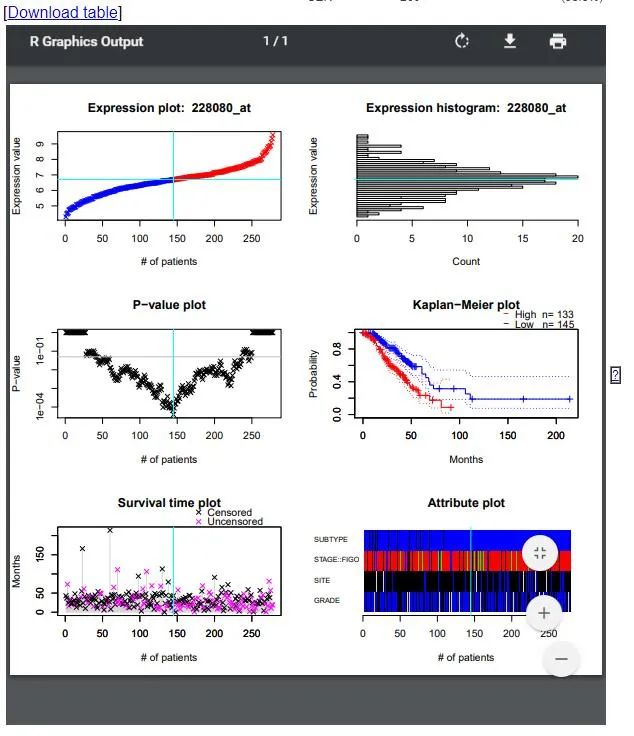
但是PrognoScan数据库的优势在于数据来源,是GEO而不是TCGA,因为TCGA的生存分析工具已经非常多。
为什么图好糊啊
Kaplan-Meier (KM) Plotter的疾病亚型要么是全部,要么是单个,怎么多选/自选疾病类型呀,还是要自己去下载原始数据再分析?
emmm,可以问个对于我很基础的问题吗?想请教下老师,非癌症,想分析的的非癌症的生存分析,可以用这些平台吗?
您好,这个GSE数据做出来的生存分析可以放到文章里吗?
可以哇,引用这个工具就好
我的也不行,遇到跟你一样的情况
确实,早知道先把他的数据保存下来了 自己建个工具也行哇
你好,我想请问一下为什么这个网站现在用不了了吗还是我这边的问题吗
我用edge和火狐浏览器都试过了,edge直接进不去官网,火狐进去之后输入基因名称就连接超时了试过很多次了是什么原因呢
连接超时
dna00.bio.kyutech.ac.jp 的服务器响应时间过长。
此站点暂时无法使用或者太过忙碌。请过几分钟后再试。
如果您无法载入任何网页,请检查您计算机的网络连接状态。
如果您的计算机或网络受到防火墙或者代理服务器的保护,请确认 Firefox 已被授权访问网络。
前几天我还可以用的 现在确实打不开了。。。